
|
https://www.eflm.eu/upload/newsletters/2019-Jan-Feb-EuroLabNews.pdf Каждый квадратный дюйм поверхности нашего тела, от нашей кожи до эпителия нашего кишечника, заполнен динамическим микробным сообществом, состоящим из бактерий, архей, грибов, простейших и вирусов. Этот микроскопический мир все вместе называют микробиотой или микробиомом. Как первый слой нашей самой интимной среды, неудивительно, что микробиом оказывает влияние на наше здоровье и болезни. Действительно, все больше и больше исследований показывают, что все большее число заболеваний связано с изменениями в микробиоме (Young 2017). Хотя изучение таких отношений все еще находится в зачаточном состоянии, микробиом влечет за собой обещание предоставить новые возможности для медицины. Во-первых, даже если причинно-следственная связь неясна, простое обнаружение существенной корреляции изменений микробиома с болезненным состоянием может проложить путь для разработки новых диагностических инструментов. Усилия в этом направлении направлены на такие заболевания, как рак, которые были выявлены на ранней стадии. значительно увеличит шансы на успешное лечение (Garrett 2015). Во-вторых, если изменения микробиома являются одними из причин прогрессирования заболевания или связаны с некоторыми из нежелательных симптомов, то вмешательства в микробиом могут представлять новую возможность лечения. Селективные антибиотики, пребиотики (соединения, способствующие росту определенных полезных микробов) или пробиотики (продукты питания или продукты, содержащие полезные микробы) являются возможными способами изменения микробного состава определенных ниш. В конечном счете, идея полной трансплантации микробиома от здорового донора реципиенту была успешно реализована для кишечника (Borody and Khoruts 2012). Чтобы распутать связь микробиома с нашим здоровьем и болезнью, необходимо тщательно изучить, что такое «здоровый» микробиом и как он может изменяться в зависимости от таких параметров, как возраст, диета или привычки. За последнее десятилетие или около того были предприняты значительные усилия для понимания того, каковы параметры нормальности у здоровых людей и как это изменяется при болезненных состояниях. В целом, большинство исследований показали, что межиндивидуальная изменчивость может быть очень высокой, и что влияние окружающей среды, такое как диета, имеет тенденцию быть более важным, чем географическое происхождение или генетический фон. Разнообразие микробных сообществ, обнаруженных в популяциях человека, иногда можно сгруппировать в так называемые экотипы, такие как энтеротипы в кишечнике (Arumugam et al. 2011) или стоматологические типы во рту (Willis et al. 2018). Вместо дискретных стабильных категорий, таких как группы крови, экотипы микробиомов должны рассматриваться как динамические равновесия, разделенные градиентами промежуточных композиций (Knights et al. 2014). Кроме того, эти широкие классификации, как правило, определяются доминирующими наиболее многочисленными видами, и можно найти много различий в отношении состава менее распространенных видов. Многие исследования обнаружили корреляцию между численностью определенных видов и изменениями в рационе питания или привычками. Такие корреляции часто включают виды от средней до низкой численности и, как правило, их трудно интерпретировать с точки зрения причинно-следственных связей. Что касается изменений микробиома при болезненных состояниях, то одной общей темой является дисбактериоз или измененный эквилибрий. О таком дисбиозе часто свидетельствует потеря биоразнообразия в микробиоме, при котором в большей части популяции преобладает один или несколько видов. Напротив, здоровые микробиомы, как правило, имеют более высокие индексы биоразнообразия, с большим количеством видов, с более сбалансированными пропорциями. Особый интерес для клинической лаборатории представляет то, как состав микробиома может быть таким, каким он был, хотя микробиом был тщательно изучен в течение прошлого столетия с помощью традиционных методов, таких как микроскопия, и методов, основанных на культивировании, они строго ограничены. Лишь недавно достижения в технологиях секвенирования позволили нам получить быстрый, практически беспристрастный, экономичный и всесторонний доступ к составу микробиома. Эти методы, которые в совокупности часто называют «метагеномикой», могут быть разными, в зависимости от того, как они нацелены. Краткое изложение основных подходов приведено в таблице ниже. Вкратце, такие методы начинаются с выделения ДНК, содержащейся в интересующем образце. Какой тип образца и как его получают, очень важен, так как различия в протоколах отбора образцов могут привести к различиям в исследованиях, проведенных в разных лабораториях. Например, оральный мазок, образец мокроты и промывание полости рта могут сообщать информацию о микробиоме полости рта, но они будут действовать иначе. Зачастую исследование или клинический вопрос определяют, какой тип образца является наиболее подходящим. После извлечения ДНК доступно несколько вариантов. Наиболее беспристрастный подход к анализу этой ДНК заключается в использовании метагеномного подхода с использованием дробовика, при котором все содержание ДНК в образце разрезается, секвенируется и анализируется. Разрешение, которое может быть обеспечено этим подходом, очень высоко. Полные геномы для наиболее распространенных видов могут быть собраны, и можно получить информацию даже на уровне штамма. Кроме того, поскольку образцы из всего генома отбираются, становится возможным получить не только наиболее вероятную таксономическую принадлежность каждой анализируемой последовательности, но также и то, какие белки кодируются, что обеспечивает информацию о функциональном потенциале. Если функциональное профилирование является основной целью, альтернативный подход заключается в использовании метатранскриптомики, которая нацелена на молекулы РНК в образце, а не на ДНК, таким образом предоставляя информацию о том, какие пути активно экспрессируются. Наконец, более целенаправленные подходы, такие как метабаркодирование, позволяют амплифицировать конкретную область ДНК с помощью «универсальных» праймеров. Такие метабаркодированные подходы являются наиболее экономически эффективными, если относительная пропорция различных таксонов является интересующим параметром. Ivan Denisov 03 Feb 2019 11:59 PIT00368 Микробиомы разные Микробиомы не просто разные! Действие антибиотиков на микрофлору кишечника и обмен веществ зависит от принимающего антибиотики. Действие антибиотиков очень индивидуально и сильно зависят от генетики человека. Это показано в недавней работе {Fujisaka2016} Shiho Fujisaka, Siegfried Ussar, Clary Clish, Suzanne Devkota, Jonathan M. Dreyfuss, Masaji Sakaguchi, Marion Soto et al. Antibiotic effects on gut microbiota and metabolism are host dependent // The Journal of Clinical Investigation 126 (12), 4430-4443 (2016). doi 10.1172/JCI86674 В расширенном реферате один микробиомом не подходит для всех популярно рассмотрена результаты статьи [Fujisaka2016]. Заменю пересказ простым напоминанием, того, что когда едите, не забывайте о родословной, т.к. точной характеристики связи результатов действия антибиотиков, ожирения и диабета с генетическим паспортом пока не удалось установить. Хотя зависимость от генетики в работе [Fujisaka2016] доказана. Тот факт, что в иммунной системе все микробиомы разные хорошо известен. А вот что хорошо для одного, может быть плохим для другого в зависимости от родословной, с этим нельзя не считаться. Пока не ясна генетика нельзя действовать на микробиом одними и теми же лекарствами. Действительно, индивидуальная медицина нужна. А вот насколько микробиомы разные? Чтобы не расслабляться, задайтесь вопросом, как микробиомы влияют друг на друга. Для того, чтобы исследовать, как микробиом адаптируется к новой среде, обратим внимание на приматов. В работе [Clayton2016] изучена микрофлора из двух видов обезьян, живущих в зоопарке, в храме, или в дикой природе. Данные показали, что у обезьян, живущих в дикой природе широкое разнообразие микробиомов, в то время как животные, живущие в святилищах показали значительно меньшее разнообразие. Интересно, что обезьяны, живущие в зоопарках, показали еще меньше разнообразия, а их микробиомы на самом деле напоминают найденные у современных людей. Последующее исследование 33 обезьян, представляющих 8 различных видов, взятые из зоопарков показали аналогичную микробную комплементарность. {Clayton2016} Jonathan B. Clayton, Pajau Vangay, Hu Huang, Tonya Ward, Benjamin M. Hillmann, Gabriel A. Al-Ghalith, Dominic A. Travis et al. Captivity humanizes the primate microbiome // Proceedings of the National Academy of Sciences 113 (37), 10376–10381 (2016). doi 10.1073/pnas.1521835113 Peter Belobrov 06 Dec 2016 02:38 PIT00358 Микробиом глаз За 4 года это седьмой пост по поводу микробиома в ряду PIT00008, PIT00010, PIT00271, PIT00297, PIT00315 и PIT00349. Изменения микробиома глаз, связанные с ношением контактных линз, описаны в статье {Shin2016} Hakdong Shin, Kenneth Price, Luong Albert, Jack Dodick, Lisa Park, and Maria Gloria Dominguez-Bello. Changes in the eye microbiota associated with contact lens wearing // mBio 7 (2), e00198-16 (2016). doi 10.1128/mBio.00198-16 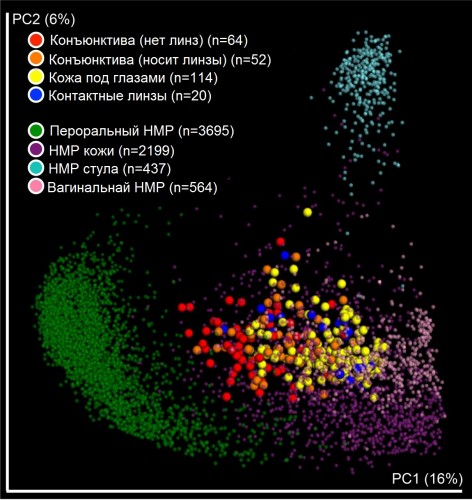 Рис.3 [Shin2016] Бета разнообразие в образцах конъюнктивы, кожи и контактных линз в сравнении с образцами из базы данных HMP (Human Microbiome Project = Проект микробиома человека). Участок PCoA был сгенерирован с использованием невзвешенных расстояний UniFrac. Маленькие точки (зеленый, фиолетовый, голубой и розовый) указывают на образцы из базы данных HMP и большие точки (красный, оранжевый, желтый и синий) показывают образцы этого исследования. Грамотное популярное объяснение того, почему контактные линзы могут изменить микробиом глаза написано в журнале BioTechniques 30/3/2016 Проект микробиома человека преподносит постоянно сюрпризы. Ниже список литературы из поста PIT00010 с добавлением числа цитирований на 24/11/2016 Y K Lee, S K Mazmanian. Has the Microbiota Played a Critical Role in the Evolution of the Adaptive Immune System? // Science 330 (6012), 1768-1773 (2010). Cited by 557 (# ) mib205 P R Hirsch & T H Mauchline. Who's who in the plant root microbiome? // Nature Biotechnology 30, 961–962 (2012). Cited by 38 (# ) mib206 D S Lundberg et al. Defining the core Arabidopsis thaliana root microbiome // Nature 488, 86–90 (2012). Cited by 455 (# ) mib207 D Bulgarelli et al. Revealing structure and assembly cues for Arabidopsis root-inhabiting bacterial microbiota // Nature 488, 91–95 (2012). Cited by 380 (# ) mib208 A A Gust & T Nurnberger. Plant immunology: A life or death switch // Nature 486, 198–199 (2012). Cited by 13 (# ) mib209 Z Q Fu et al. NPR3 and NPR4 are receptors for the immune signal salicylic acid in plants // Nature 486, 228–232 (2012). Cited by 304 (# ) mib210 Дж Аккерман. Древнейшая социальная сеть // В мире науки, № 8, 10-17 (2012). J Ackerman. The Ultimate Social Network // Scientific American 306 (6), 36-43 (2012). Cited by 35 (# ) mib211 J Qin at al. A human gut microbial gene catalogue established by metagenomic sequencing // Nature 464, 59-65(2010). Cited by 4097 (# ) mib212 J V Weinstock. Autoimmunity: The worm returns // Nature 491, 183–185 (2012). Причины есть червей. Джоэл В. Вайншток объясняет как новые исследования с помощью кишечных паразитов указывают на потенциально новые методы лечения аутоиммунных заболеваний. Cited by 52 (# ) mib213 E A Grice and J A Segre. The Human Microbiome: Our Second Genome // Annual review of genomics and human genetics 13, 151-170 (2012). Cited by 121 (# ) mib214 The Human Microbiome Project Consortium. Structure, function and diversity of the healthy human microbiome // Nature 486, 207–214 (2012). Cited by 1997 (# ) mib216 The Human Microbiome Project Consortium. A framework for human microbiome research // Nature 486, 215–221 (2012). Cited by 681 (# ) mib217 J Shendure & E L Aiden. The expanding scope of DNA sequencing // Nature Biotechnology 30, 1084–1094 (2012). Cited by 190 (# ) mib218 S A Slavoff & A Saghatelian. Discovering ligand-receptor interactions // Nature Biotechnology 30, 959–961 (2012). Cited by 5 (# ) mib219 A P Frei et al. Direct identification of ligand-receptor interactions on living cells and tissues // Nature Biotechnology 30, 997–1001 (2012). Cited by 55 (# ) mib220 M Isalan. Systems biology: A cell in a computer // Nature 488, 40–41 (2012). Cited by 13 (# ) mib221 J R Karr at al. A Whole-Cell Computational Model Predicts Phenotype from Genotype // Cell, 150 (2), 389–401 (2012). Cited by 594 (# ) mib222 P L. Freddolino, S Tavazoie. The Dawn of Virtual Cell Biology // Cell, 150 (2), 248-250 (2012). Cited by 18 (# ) mib223 Peter Belobrov 24 Nov 2016 00:30 PIT00349 Качество жизни зависит от микробиома Уже 4 года обсуждаются различные микробиомы (нажмите #микробиом после заголовка, чтобы посмотреть все посты по данной теме) на этом сайте. Новое исследование раскрывает возможную роль, которую играет наш микробиомом для здорового качества жизни, в частности при старения и долголетии. Fanli Kong, Yutong Hua, Bo Zeng, Ruihong Ning, Ying Li, and Jiangchao Zhao. Gut microbiota signatures of longevity // Current Biology 26 (18), R832-R833 (2016). doi 10.1016/j.cub.2016.08.015 Эта работа популярно обсуждается в тексте Конечно, понятен интерес к долголетию, хотя самые интересные новости идут из мира хороших вирусов и бактерий, которые выполняют едва ли не самую главную функции в поддержании здоровой жизни всей биосферы, включая, конечно и человека. Maureen A. O'Malley. The ecological virus // Studies in History and Philosophy of Science Part C: Studies in History and Philosophy of Biological and Biomedical Sciences 59, 71-79 (2016). doi 10.1016/j.shpsc.2016.02.012 Thomas Pradeu, Gladys Kostyrka, and John Dupré. Understanding viruses: Philosophical investigations // Studies in History and Philosophy of Science Part C: Studies in History and Philosophy of Biological and Biomedical Sciences 59, 57-63 (2016). doi 10.1016/j.shpsc.2016.02.008 На русском языке очень хорошо понимание роли вирусов в биологическом разнообразии рассмотрено в учебнике Пиневич А.В., Сироткин А.К., Гаврилова О.В., Потехин А.А. Вирусология. Учебник. Санкт-Петербургский университет. 2012. 434 с. Книгу можно скачать свободно, правда без текстового слоя.
Аннотация. Книга выходит на фоне острого дефицита отечественных и полного отсутствия переводных руководств по вирусологии. В ней вирусы предстают не только как болезнетворные агенты, но и как глобальный компонент биологического разнообразия, играющий огромную роль в биоценозах и занимающий ключевое место в органической эволюции. Рекомендую познакомиться с этой книгой. Даже после беглого прочтения вам никогда не придёт в голову говорить глупости о том, что все вирусы плохие. Понимание роли вирусов в биологическом разнообразии у вас будет более ясным. Картина того, как биологическое разнообразие обеспечивает непрерывность жизни при конечном пространственно-временном существовании всех живых существ будет у вас красочной, насыщенной и правильной. Ваши представления будут тогда соответствовать действительно прекрасному явлению - жизнь. Peter Belobrov 18 Oct 2016 06:14 Лугдунин - 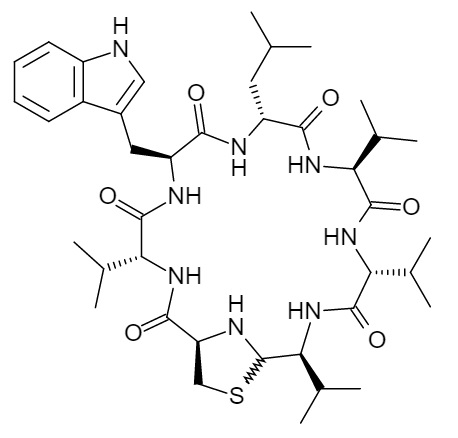 Alexander Zipperer et al. Human commensals producing a novel antibiotic impair pathogen colonization // Nature 535 (7613), 511-516 (2016). doi 10.1038/nature18634 Команда Пешеля (Andreas Peschel) теперь планирует выяснить, могут ли лугдунин или микробы, которые производят его, быть использованы для разработки новых методов лечения. "Мы находимся в самом начале разработки концепции", заключил Пешель. Ниже приведена картинка и небольшой текст с его сайта. 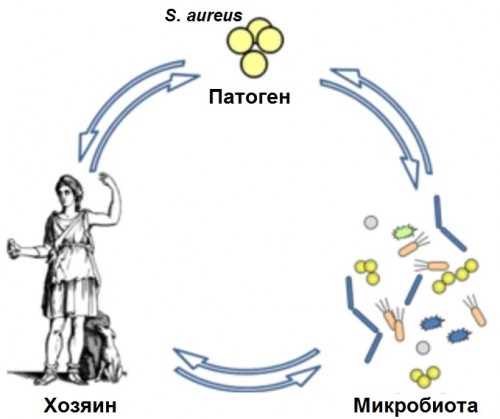 Несмотря на важность микробной экологии поверхность человеческого тела практически не были изучены. Человеческая кожа и слизистые оболочек носа заселены бактериями рода Staphylococcus некоторые из которых представляют собой основные человеческие патогены. Золотистый стафилококк Staphylococcus aureus наиболее патогенный вид, чаще всех развивает резистентность к существующим антибиотикам, что часто приводит к едва поддающиеся лечению инфекциям. Изучение механизмов колонизации и инфекции наряду с новыми способами профилактики и лечения стафилококковых заболеваний представляют главные исследовательские цели отдела Пешеля. Стоит заметить, что среди хороших и плохих стафилококков надо ещё разбираться. Несомненно одно. Симбиотические взаимодействия клеток человека с клетками микробиома очень непростые. Поэтому проблема многоуровневых коллективных биологических взаимодействий тканей, клеток, веществ, синтезируемых клетками, и субклеточных органелл требует точного решения. Нос человека открывает новую антибиотическую эру - названа статья, которая содержит дополнительные ссылки, в журнале BioTechniques с информацией об открытии лугдунина группой Пешеля. Hannah Martin Lawrenz. The Human Nose Pilots a New Antibiotic Era Peter Belobrov 01 Sep 2016 13:56 PIT00297 Gut-Brain Interaction Gut-Brain Interaction = Взаимодействие кишечника с мозгом! Для тех, кто знает о гемато-энцефалическом барьере (ГЭБ) или blood–brain barrier (BBB) это звучит оксюмороном. ГЭБ защищает нервную ткань от циркулирующих в крови микроорганизмов, токсинов, клеточных и гуморальных факторов иммунной системы, которые воспринимают ткань мозга как чужеродную. Тем не менее достойна вашего внимания новость. О последнем "выкрутасе" влияния бактерий на мозг хозяина новое исследование, которое показывает, что кишечные микробы вызывают симптомы отчаяния, и микробные популяции могут быть также ответственны за возникновение и развитие рассеянного склероза. References 1. Mar Gacias et al. Microbiota-driven transcriptional changes in prefrontal cortex override genetic differences in social behavior // eLife 5, e13442 (2016), doi 10.7554/eLife.13442. 2. Sushrut Jangi et al. Alterations of the human gut microbiome in multiple sclerosis // Nature Communications 7, 12015 (2016), doi 10.1038/ncomms12015. 3. Jia Liu et al. Clemastine enhances myelination in the prefrontal cortex and rescues behavioral changes in socially isolated mice // The Journal of Neuroscience 36 (3), 957-962 (2016), doi 10.1523/JNEUROSCI.3608-15.2016. Ключевые слова: микробиомом, множественный склероз, аутоиммунная микроскопия, 16S рРНК, секвенирование, метагеномика, метаболомика, транскриптомика, миелин Keywords: microbiome, mutliple sclerosis, autoimmune microscopy, 16S rRNA, sequencing, metagenomics, metabolomics, transcriptomics, myelin Peter Belobrov 28 Jul 2016 13:26 PIT00271 Контроль микробиомов хозяином С биологической точки зрения, точного ответа на вопрос "кто в теле хозяин?" - нет! Но с исторической или социальной точки зрения часто предполагают в гипотезе стволового развития, что более сложный объект хозяин для менее сложного. С точки зрения сетевого развития симбиозов хозяина никогда нет. Есть даже более сильное утверждение, что биологическим хозяином в симбиозе является самый опытный и самый "пронырливый" участник симбиоза, т.е. E.coli и "иже с ними". Не будем пока заморачиваться на этом. Свежая новость {Liu2016} Shirong Liu, Andre Pires da Cunha, Rafael M. Rezende, Ron Cialic, Zhiyun Wei, Lynn Bry, Laurie E. Comstock, Roopali Gandhi, and Howard L. Weiner. The Host Shapes the Gut Microbiota via Fecal MicroRNA // Cell host & microbe 19 (1), 32-43 (2016). doi 10.1016/j.chom.2015.12.005 (сама статья пока никак недоступна!) "с колёс" рассмотрена в BioTechniques Kristie Nybo. How Hosts Control Their Microbiomes где приведен рисунок из аннотации статьи [Liu2016] 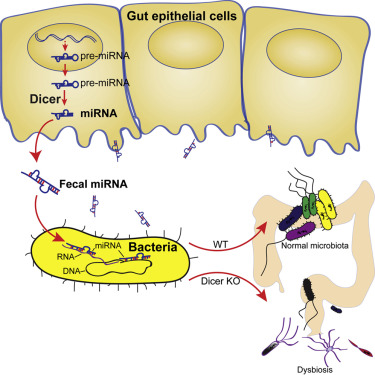 и сказано следующее. Так как микробы кишечника играют важную роль в обмене веществ, в иммунитете и при болезнях, важно понять механизмы, с помощью которых микрофлора регулируется хозяином, и определить пути, которыми можно манипулировать микробиомом. Предыдущие исследования показали, что кишечные микробы, пересаженные из рыбы в зародыши мышей, скорее напоминает нормальную микрофлору мыши, что указывает на то, что мышиный зародыш формирует состав своих кишечных бактерий. Вайнер (Weiner) и его коллеги задались целью выяснить, как это происходит, и сообщили в журнале [Liu2016] следующее. "Наши результаты показывают, что механизм защиты организма состоит в выделении микроРНК в качестве стратегии для манипуляций микробиомом для здоровья хозяина", сказал он. Команда определила, что микроРНК создаются эпителиальными клетками кишечника и бокаловидными клетками, а затем секретируется в просвет кишечника с помощью внеклеточных пузырьков. Как ни странно, взаимодействия не всегда приводят к разрушению бактериальной мРНК, как это происходит обычно для микроРНК; вместо этого микроРНК увеличили присутствие некоторых транскриптов и способствовали росту бактерий. Приведу основные моменты и аннотацию статьи, что позволяет лучше понять рисунок http://www.cell.com/cell-host-microbe/abstract/S1931-3128(15)00497-7 Highlights Summary Peter Belobrov 30 Jan 2016 06:20 Биом — классический объект экологии, но ассоциации микробиома с биномом Ньютона наводят на биоматематику... Сейчас, когда биом выходит на арену, нельзя все артефакты нам под стол мести. И потому придется нам ответственность нести за недопонимание «природа это храм». Прочтите Консорциум Микробиом человека опубликовал результаты многолетней работы и обратите внимание на слова координатора проекта Литы Проктор (Lita Proctor): «У людей нет всех ферментов, необходимых для переваривания того, что мы едим. Большая часть белков, липидов и углеводов нашего рациона расщепляется до питательных веществ, способных всасываться кишечником, микробами, которые обитают в кишечнике. Более того, микробы производят полезные вещества вроде витаминов и противовоспалительных соединений, синтез которых наш геном обеспечить не может». Собрал в кучку основные статьи по теме, название которой в имени этого поста. Ссылки с минимальным текстом отправил сегодня 12/11/12 почтой. Вот он. Литература (список, который не может оставить равнодушным никого!) Peter Belobrov 11 Nov 2012 21:01 PIT00008 Микробиом Теперь у нас к микроэмульсиям и к микрофлюидике добавился микробиом. Понимание этого пришло через пару часов после вчерашнего семинара. За выходной подберу основную литературу и сделаю полный пост PIT00010. Итак, эмульсии, флюидика, биом (который не биНом, но у Ньютона был конечно...) Peter Belobrov 11 Nov 2012 16:27
© International Open Laboratory for Advanced Science and Technology — MOLPIT, 2009–2026
|